
Insulinrezeptor
| Insulinrezeptor | ||
|---|---|---|
 | ||
|
Vorhandene Strukturdaten: s. UniProt | ||
| Eigenschaften des menschlichen Proteins | ||
| Masse/Länge Primärstruktur | 2702 = 2*731+2*620 Aminosäuren | |
| Sekundär- bis Quartärstruktur | 2α+2β single pass Rezeptor | |
| Präkursor | α+β | |
| Isoformen | Long, Short | |
| Bezeichner | ||
| Gen-Namen | | |
| Externe IDs | ||
| Enzymklassifikation | ||
| EC, Kategorie | | |
| Reaktionsart | Phosphorylierung | |
| Substrat | ATP + Protein-L-Tyr | |
| Produkte | ADP + Protein-L-Tyr-Phosphat | |
| Vorkommen | ||
| Homologie-Familie | | |
| Übergeordnetes Taxon | Chordatiere | |
| Orthologe | ||
| Mensch | Hausmaus | |
| Entrez | | |
| Ensembl | | |
| UniProt | | |
| Refseq (mRNA) | | |
| Refseq (Protein) | NP_00019 | |
| Genlocus | | Chr 8: 3.15 – 3.28 Mb |
| PubMed-Suche | | |
Der Insulinrezeptor (IR) (Gen: INSR) ist dasjenige Membranprotein, an welches ausgeschüttetes Insulin bindet und wodurch es seine Wirkung entfaltet. Der IR wird in allen Chordatieren produziert und von nahezu allen Zellen in unterschiedlicher Anzahl exprimiert. Die roten Blutkörperchen exprimieren beispielsweise nur wenige hundert Rezeptoren, Leberzellen und Fettzellen dagegen mehrere Hunderttausend. Mutationen im INSR-Gen sind verantwortlich für die vererbbare Insulinresistenz, das Rabson-Mendenhall-Syndrom, das Donahue-Syndrom, insulinunabhängiger Diabetes mellitus, familiäre Hypoglykämie und Diabetes mellitus mit Acanthosis nigricans.[1]
Struktur
Die Insulinrezeptoren sind innerhalb der Zellmembran lokalisiert und gehören somit zur Gruppe der Transmembranrezeptoren bzw. integralen Membranproteine.
Es handelt sich um ein Heterotetramer, welches aus je 2 α- und β-Untereinheiten zusammengesetzt ist: einer extrazellulären α-Untereinheit und einer die Zellmembran durchspannenden β-Untereinheit, von der sich ein großer Teil im Zellinneren befindet. Die α- und β-Untereinheiten sind jeweils durch Disulfidbrücken kovalent miteinander verbunden. Die β-Untereinheiten besitzen eine sogenannte Tyrosinkinase-Aktivität. Das heißt, dass sie in der Lage sind, Tyrosinreste zu phosphorylieren. Die Phosphatgruppe stammt dabei von einem ATP-Molekül.[2]
Insulinbindung und Autophosphorylierung
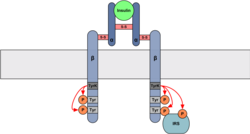
Wenn ein Insulinmolekül von den beiden α-Untereinheiten gebunden wird, kommt es zu einer Konformationsänderung. Die beiden β-Untereinheiten nähern sich einander an und phosphorylieren sich gegenseitig. Daher handelt es sich um eine trans-Autophosphorylierung. Die Kinase-Domänen der β-Untereinheiten erfahren durch die Phosphorylierung eine Konformationsänderung und werden dadurch aktiviert.[2]
Hat die Tyrosinkinase des Insulin-Rezeptors nach Insulinbindung und Aktivierung ihren aktiven Zustand eingenommen, werden mehrere Rezeptoruntereinheiten nahe der Kinasedomäne phosphoryliert und stellen nun Bindungsstellen für intrazelluläre Substrate (z.B. Insulinrezeptorsubstrate, IRS) dar. IRS sind sog. Adapterproteine zwischen dem Insulinrezeptor und dem Protein, das die Signalkaskade weiterleitet (z.B. Phosphoinosidkinase-3).[2]
Weiterhin findet innerhalb weniger Minuten eine Endozytose des gesamten Bereichs statt, wodurch die Kinaseaktivität des Rezeptors ins Zytosol getragen wird. Nach getaner Wirkung wird der Rezeptor recycliert.[3][4]
Letztlich löst die Bindung von Insulin an seinen Rezeptor mehrere Kinase-Kaskaden (Kaskade von Phosphorylierungsreaktionen) aus, die durch Signalwege beschrieben werden können.[2]
Aktivierte Signalwege
Das Insulinsignal wird durch die Bildung von Signalkomplexen an verschiedene intrazelluläre Signalkaskaden gekoppelt. Diese Signalwege stoßen vielfältige Prozesse in der Zelle an, wie beispielsweise die rasche Glucoseverarbeitung, die Lipid- und Protein-Verstoffwechselung, wie auch die dazu notwendige Genexpression.[5]
MAP-Kinasekaskade
Dieser Weg aktiviert die Proteinsynthese über die Phosphorylierung des SHC-transforming Protein, SOS-GRB2-modulierte Aktivierung von Ras und nachfolgend Raf, und anschließender MAP-Kinase-Kaskade.[6][7][8]
Insulinrezeptor-Substrat-Kaskade
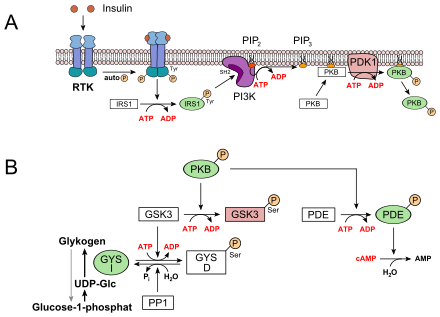
Über oben genannte IRS-Adapterproteine wird die Phosphoinositid-3-Kinase aktiviert, was wiederum zur PI3-Kaskade mit Aktivierung von Proteinkinase B (PKB) führt, welches mehrere Zielproteine phosphoryliert. Phosphorylierung der Glykogensynthase-Kinase 3 deaktiviert sie, wodurch laufende Phosphorylierung der UDP-Glykogensynthase unterbleibt, wodurch diese aktiviert wird. Mögliche Phosphorylierung der Insulin-stimulierte Proteinkinase (ISPK, RSK2) phosphoryliert und aktiviert die Proteinphosphatase PP1G. PP1G dephosphoryliert Glykogenphosphorylase, die hierdurch wiederum deaktiviert wird. Durch diesen Vorgang wird Glucose (bei hoher Energieladung) dem Glykogenspeicher zugeführt.[8][9]
PKB bewirkt außerdem, dass Vesikel mit dem sonst auf der Zelloberfläche nicht vorhandenen Glucose-Transporter 4 (GLUT4) mit der Zellmembran in Muskel- und Fettzellen verschmelzen. Dadurch wird GLUT4 funktionsfähig und es kann Glukose vermehrt für die Energiegewinnung herangezogen werden. Über diesen Mechanismus wird der Blutglukosespiegel rasch und effektiv gesenkt. Aber GLUT4 wird auch noch über einen anderen Weg aktiviert.[8]
SH2-Adapterprotein-Kaskade
Die Phosphorylierung von SH2-Adapterprotein 2 (APS) und weitere Aktivierung von Cbl, GRF2, Tc10, CIP4/2 verstärkt die Mobilisierung von GLUT4-Vesikeln mit folgendem massivem Import von Glukose in die Zelle.[8]
Die geschilderten Wege bewirken also ein Sinken des Blutglucosespiegels durch
- Förderung der Glucose-Aufnahme (GLUT4-Translokation zur Zelloberfläche)
- Förderung der Glucose-Speicherung (Glykogen-Synthese) in der Leber und den Muskeln
Dieses Signal wird durch Anschalten Glucose-verbrauchender Wege unterstützt. Weitere unterstützende Maßnahmen bestehen im Abschalten Glucose-liefernder Wege, so zum Beispiel durch Abbau des second messenger cAMP über eine Phosphodiesterase (PDE).
Recycling des internalisierten Rezeptors
Das an Insulin gebundene phosphorylierte Rezeptormolekül befindet sich in einem im Zytosol schwimmenden Vesikel, dessen Endozytose nach fünf Minuten abgeschlossen ist. Im Vesikel befinden sich außer Protonenpumpen bereits insulinabbauende Enzyme. Durch die Protonenpumpen senkt sich der pH im Vesikel von 7,4 auf 6,0, wodurch sich das Insulin vom Rezeptor trennt und abgebaut wird. Nachdem kein Insulin mehr das Signal aufrechterhält, sind Protein-Tyrosin-Phosphatasen in der Lage, den Rezeptor zu dephosphorylieren. Saures Milieu veranlasst das Vesikel schließlich, sich mit dem recyclierten Rezeptor wieder in die Zellmembran zu integrieren.[10]
Einzelnachweise
- ↑ UniProt
 P06213
P06213 - Hochspringen nach: 1 2 3 4 Stryer, Biochemie (6. Aufl.), Spektrum-Verlag
- ↑ AP Bevan/reactome.org:
 Internalisation of the insulin receptor
Internalisation of the insulin receptor - ↑ AP Bevan/reactome.org:
 Insulin receptor recycling
Insulin receptor recycling - ↑ Saltiel AR, Kahn CR: Insulin signalling and the regulation of glucose and lipid metabolism Nature. 2001 Dec 13;414(6865):799-806.
 PMID 11742412
PMID 11742412 - ↑ reactome.org:
 SHC-related events triggered by IGF1R
SHC-related events triggered by IGF1R - ↑ Nasi/Annibali/reactome.org:
 ERK/MAPK targets
ERK/MAPK targets - Hochspringen nach: 1 2 3 4
 KEGG: Insulin Signaling pathway
KEGG: Insulin Signaling pathway - ↑ reactome.org:
 IRS-related events triggered by IGF1R
IRS-related events triggered by IGF1R - ↑ AP Bevan/reactome.org:
 Insulin receptor recycling
Insulin receptor recycling


© biancahoegel.de
Datum der letzten Änderung: Jena, den: 26.04. 2026